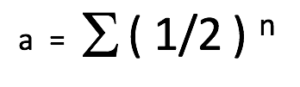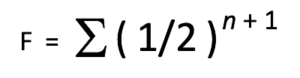Les races modernes de nos chiens sont presque toutes par définition des groupes d’animaux consanguins. Le nombre limité des animaux fondateurs pour une race pure, les livres de généalogie fermés et la tendance à utiliser seulement une fraction des animaux d’une race pour produire la prochaine génération (« effet de champion » et « effet de mâle populaire ») font que nos races pures de chiens sont composés d’animaux consanguins.
Le coefficient de relation (a) et le coefficient de consanguinité (COI)
En 1921-1922, Sewall Wright, un généticien et mathématicien américain, a défini deux valeurs mathématiques basées sur un pédigrée connu : le coefficient de relation (a) et le coefficient de consanguinité (COI ou parfois simplement « F »). Ces deux valeurs peuvent être utiles lorsqu’on veut prendre des décisions au sujet de l’accouplement des animaux domestiques. Ces coefficients ne sont pas des valeurs absolues et elles ne représentent qu’indirectement l’ADN et les gènes de l’animal. Ce sont des valeurs abstraites calculées, faites avec la supposition que tous nos gènes ont une hérédité mendélienne simple avec des allèles dominants et récessifs, ce qui est parfois simpliste. Même si ce sont des chiffres abstraits, le coefficient de relation et le coefficient de consanguinité sont des mesures utiles avec des applications pratiques. Ils permettent d’estimer la relation génétique entre deux animaux ainsi que la variation génétique dans le génome d’un animal en particulier. Ainsi, les éleveurs peuvent estimer les risques d’effets indésirables sur la santé (dépression de consanguinité) des générations futures en raison de l’absence de variation génétique due à trop de consanguinité.
Le coefficient de relation (a) est une estimation de la quantité d’ADN qui est partagée entre deux animaux dans un pédigrée. La formule le plus simple qui exprime ce coefficient est la suivante :
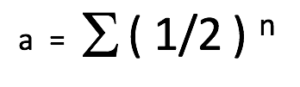
Où :
a = le coefficient de relation entre deux animaux
½ = la contribution génétique d’un parent vers son enfant
n = le nombre de chemins (ou nombre de générations) qui sépare les deux animaux dans le pédigrée. Autrement dit, le nombre de méioses (division cellulaire des cellules sexuelles) dans la lignée génétique ou le nombre de fois que le sexe productif s’est passé entre les deux animaux en question.
Σ = la somme des calculs pour toutes les voies possibles reliant les deux individus
Cette équation découle du fait que nous (et nos chiens) sommes diploïdes et donc que nous avons reçu la moitié de notre l’ADN de notre mère et l’autre moitié de notre père. Autrement dit, l’ADN de nos parents a été divisé en deux (½) puis additionné (½ + ½ = 1,0) pour nous générer et créer notre propre ADN. Si deux animaux ne sont pas liés génétiquement, leur coefficient de relation est de 0. Au contraire, si deux animaux sont liés génétiquement (avec parents ou ancêtres communs) leur coefficient de relation sera supérieur à 0 et peut être calculé.
Le coefficient de consanguinité (COI, parfois dit « F ») est une estimation de la perte de variation génétique chez un animal donné, du fait de son ancêtre commun, tant du côté paternel que du côté maternel de son pedigree. Le coefficient de consanguinité peut être calculé à partir du coefficient de relation avec la formule suivante :
COI = (1/2) a = (1/2) n+1
Une présentation plus complète de la formule du coefficient de consanguinité est la suivante :
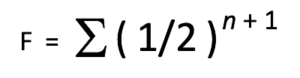
Où :
F = le coefficient de consanguinité (COI) pour l’individu en question.
½ = la contribution génétique d’un parent vers son enfant.
n = le nombre de chemins (ou nombre de générations) qui sépare les deux parents d’un individu à partir d’un ancêtre commun.
+1 = un facteur supplémentaire de (1/2) est ajouté pour représenter la perte moyenne de diversité génétique due à des ancêtres communs des côtés maternel et paternel de l’arbre généalogique.
∑ = la somme des calculs pour chaque ancêtre individuel en commun.
Si l’ancêtre en commun a lui-même des ancêtres en communs, alors il aura alors une valeur de coefficient de consanguinité positive. Le coefficient de consanguinité de l’animal en question est maintenant multiplié par le facteur de correction suivant:
(1 + Fa)
Où :
Fa = le coefficient de consanguinité de l’ancêtre en commun.
Pour les individus intrépides et les masochistes de la mathématique, les formules peuvent être plus complexe encore :
http://www.genetic-genealogy.co.uk/Toc115570144.html
http://www.genetic-genealogy.co.uk/Toc115570148.html.
Quelques exemples de coefficients de relation et de coefficients de consanguinité
Voici quelques exemples de coefficients de relation (la moyenne d’ADN commun) entre deux êtres apparentés qui n’ont aucun ancêtre commun. Le coefficient de consanguinité pour leur progéniture hypothétique est aussi calculé.
| Relation de parenté |
Coefficient de relation (a) |
Coefficient de consanguinité (COI)
de leur progéniture
|
| Parent – enfant |
50% |
25% |
| Frère – sœur |
50% |
25% |
| Grand-parent – petit-enfant |
25% |
12,5% |
| Oncle/tante – neveu/nièce |
25% |
12,5% |
| Demi-frère – demi-soeur |
25% |
12,5% |
| Cousin – cousine |
12,5% |
6,25% |
| Demi-cousins |
6,25% |
3,125% |
| Deuxième cousin |
3,13% |
1,063% |
Voici un exemple : un enfant et son parent partage 50 % de leur génétique, alors le coefficient de relation (a) est 50 %. L’enfant a un coefficient de consanguinité de 0. Un enfant issu du croisement entre un parent et son enfant ou entre un frère et une sœur aura un coefficient de consanguinité de 25%. Ça veut dire qu’en moyenne il y aura une perte de 25% de variation génétique (perte de M/N) et un gain de 25 % d’uniformité génétique (gain de N/N, M/M) au niveau de l’ADN de l’enfant. Les croisements proches soit entre un parent et son enfant ou entre un frère et une sœur sont maintenant interdits par certaines associations comme « The Kennel Club (d’Angleterre) ». Cependant, ils sont encore permis par d’autres associations. En ce qui concerne les humains, le mariage entre cousins est permis dans certains pays, même si leur descendance aura un coefficient de consanguinité de 6,25 %.
The Kennel Club (d’Angleterre) – la valeur moyenne des coefficients de consanguinité
The Kennel Club (www.thekennelclub.org.uk) calcule la valeur moyenne actuelle des coefficients de consanguinité (COI) pour une race de chien donnée. Ces valeurs sont basées sur les pedigrees des chiots du Royaume-Uni enregistrés par « The Kennel Club » pour une race donnée au cours de l’année précédente.
Sur la base des calculs du The Kennel Club, voici quelques exemples de coefficients de consanguinité moyens basés sur les pedigrees de plusieurs races de chiens au Royaume-Uni, pour 2019:
| Race |
COI (%) |
Race |
COI (%) |
| Airedale Terrier |
17,6 |
Épagneul breton |
5,7 |
| Yorkshire Terrier |
11,3 |
Terre-Neuve |
5,0 |
| Épagneul cocker anglais |
10,7 |
Retriever de la Baie de Chesapeake |
3,4 |
| Staffordshire Bull Terrier |
9,5 |
Shar Pei |
3,0 |
| Beagle |
8,6 |
Berger australien |
2,9 |
| Labrador Retriever |
6,6 |
Berger allemand |
2,8 |
| Teckel à poil dur |
6,6 |
Retriever de la Nouvelle-Écosse (NSDTR) |
1,6 |
| Bullmastiff |
5,9 |
Eurasier |
1,0 |
Pour une liste plus complète, vous pouvez consulter la page chez Labgenvet sur la :
Génétique du chien 4.2 : Coefficients de consanguinité basés sur les pedigrees des races de chiens, tels que calculés et fournis par The Kennel Club, pour 2019.
Consanguinité et la perte de diversité génétique
Encore une fois, pour un coefficient de consanguinité de 10%, cela signifierait que pour les sites génétiques hétérozygotes (M/N, porteurs) chez un ancêtre commun, il y a 10% de chance que ces locus génétiques deviennent homozygotes (N/N ou M/M) chez le descendant. Autrement dit, il y a en moyenne une perte nette de diversité génétique de 10% (ou un gain d’uniformité génétique si vous voulez) dans la progéniture en raison d’accouplements impliquant une consanguinité. Un locus génétique particulier qui a été converti d’hétérozygote (diversité) en homozygote (uniformité) chez une progéniture est engendré par la consanguinité dont celle-ci est dit identique par descendance à cause de l’ancêtre commun.
Les pédigrées
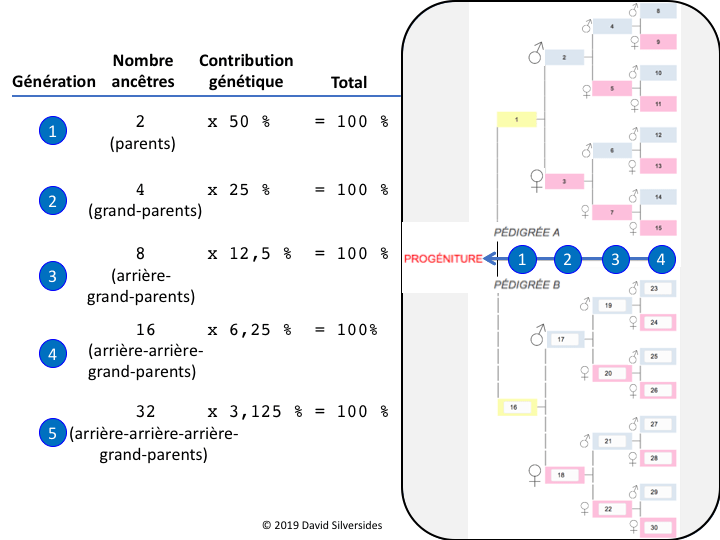
 Combien de générations d’un pédigrée doivent être prises en considération lorsqu’on calcule le coefficient de consanguinité ? La réponse est que plus il y a de générations, mieux c’est pour la validité du calcul. Utiliser un petit nombre de générations va donner une valeur de coefficient de consanguinité artificiellement basse comparé à la valeur obtenue lorsque plusieurs générations sont incluses. En pratique, lorsque l’on calcule le coefficient de consanguinité, toute l’information contenue dans le pédigrée connu est utilisée. Cette information peut être limitée à trois générations ou elle peut contenir toutes les générations jusqu’aux animaux fondateurs de la race en question.
Combien de générations d’un pédigrée doivent être prises en considération lorsqu’on calcule le coefficient de consanguinité ? La réponse est que plus il y a de générations, mieux c’est pour la validité du calcul. Utiliser un petit nombre de générations va donner une valeur de coefficient de consanguinité artificiellement basse comparé à la valeur obtenue lorsque plusieurs générations sont incluses. En pratique, lorsque l’on calcule le coefficient de consanguinité, toute l’information contenue dans le pédigrée connu est utilisée. Cette information peut être limitée à trois générations ou elle peut contenir toutes les générations jusqu’aux animaux fondateurs de la race en question.
Grace à la volonté des éleveurs et au pouvoir de l’internet, plusieurs pédigrées de nos chiens sont disponibles sur les sites dédiés aux pédigrées. Quelques exemples pour le chien sont donnés :
https://breedarchive.com/home/index
http://www.k9data.com/
Pour un animal donné, le pédigrée connu est présenté, les ancêtres communs sont notés, parfois le coefficient de consanguinité est calculé sur le nombre de générations connues. Souvent les éleveurs peuvent calculer et comparer les coefficients pour les accouplements futurs ou en d’autre mots, les accouplements virtuels.
Utilisation du coefficient de consanguinité
 Le coefficient de consanguinité, utilisé correctement, est un outil puissant pour les éleveurs quand vient le temps de choisir les parents pour les futures portées. De façon générale, un coefficient de consanguinité est une indication de l’état de santé global du génome d’un animal. Le génome est la somme totale de tous les gènes qui sont nécessaire pour la formation et la fonction de l’animal en question. Plus spécifiquement, un coefficient de consanguinité représente un pourcentage numérique basé sur une analyse de pédigrée qui reflète la perte de la variation génétique dont celle-ci se produit s’il y a des ancêtres communs sur les côtés paternel et maternel du pédigrée chez un individu, comme il a été mentionné plus haut. Avoir des ancêtres communs sur les deux côtés du pédigrée aura pour résultat d’obtenir des sites génétiques homozygotes (soit N/N ou M/M) chez les descendants à la place des sites hétérozygotes (M/N) chez les ancêtres porteurs. Cette condition est dite identique par descendance du fait d’avoir un ancêtre commun.
Le coefficient de consanguinité, utilisé correctement, est un outil puissant pour les éleveurs quand vient le temps de choisir les parents pour les futures portées. De façon générale, un coefficient de consanguinité est une indication de l’état de santé global du génome d’un animal. Le génome est la somme totale de tous les gènes qui sont nécessaire pour la formation et la fonction de l’animal en question. Plus spécifiquement, un coefficient de consanguinité représente un pourcentage numérique basé sur une analyse de pédigrée qui reflète la perte de la variation génétique dont celle-ci se produit s’il y a des ancêtres communs sur les côtés paternel et maternel du pédigrée chez un individu, comme il a été mentionné plus haut. Avoir des ancêtres communs sur les deux côtés du pédigrée aura pour résultat d’obtenir des sites génétiques homozygotes (soit N/N ou M/M) chez les descendants à la place des sites hétérozygotes (M/N) chez les ancêtres porteurs. Cette condition est dite identique par descendance du fait d’avoir un ancêtre commun.
Du côté génétique, une perte de variation génétique n’est pas désirable, car il en résulte de la « dépression de consanguinité ». La dépression de consanguinité est bien documentée chez plusieurs espèces, autant pour les animaux que pour les plantes. L’effet de la reproduction « outbreeding » ou « crossbreeding » est aussi bien documenté. Celui-ci va augmenter la variation génétique du génome d’un animal pour donner la « vigueur hybride », aussi dit l’hétérose.
 Il est important de garder en tête que le coefficient de consanguinité ne représente pas le statut de variation pour les gènes spécifiques, mais plutôt le statut de variation global et estimé pour le génome au complet. S’il n’y a pas d’ancêtres communs entre le côté paternel et le côté maternel d’un pédigrée, la progéniture n’aura aucune perte de variation génétique par rapport à une population standard. La progéniture aura alors un coefficient de consanguinité de 0. S’il y a des ancêtres communs entre le côté paternel et le côté maternel d’un pédigrée, il y a maintenant un potentiel de perte de variation génétique dans le génome de la progéniture (identique par descendance) qui peut amener à la dépression de la consanguinité.
Il est important de garder en tête que le coefficient de consanguinité ne représente pas le statut de variation pour les gènes spécifiques, mais plutôt le statut de variation global et estimé pour le génome au complet. S’il n’y a pas d’ancêtres communs entre le côté paternel et le côté maternel d’un pédigrée, la progéniture n’aura aucune perte de variation génétique par rapport à une population standard. La progéniture aura alors un coefficient de consanguinité de 0. S’il y a des ancêtres communs entre le côté paternel et le côté maternel d’un pédigrée, il y a maintenant un potentiel de perte de variation génétique dans le génome de la progéniture (identique par descendance) qui peut amener à la dépression de la consanguinité.
Le coefficient de consanguinité est maintenant un chiffre supérieur à 0, souvent exprimé en pourcentage. Il est estimé que quand la consanguinité se produit, pour chaque 1% d’augmentation dans le coefficient de consanguinité, il y a une réduction de 1 % dans les traits mesurés (dépression de consanguinité). Le coefficient de consanguinité est le plus utile pour estimer les effets de consanguinité récents.
Il n’est pas surprenant que Dame Nature aime la variation génétique, car c’est la clé à long terme pour la survie et l’évolution d’une espèce. Malheureusement, pour nos animaux domestiques, les standards de races favorisent l’élevage pour l’uniformité du phénotype (élever pour « type »). Ceci implique généralement un certain niveau de consanguinité avec l’uniformité du génotype et une variation génétique réduite comme résultat.
L’interprétation du coefficient de la consanguinité
 Une valeur de coefficient de consanguinité élevée augmentera les risques d’expression des effets nuisibles de la consanguinité (dépression de la consanguinité). Par contre, ce même coefficient de consanguinité élevé permet aussi d’augmenter les chances que les traits désirables en lien avec la race en question soient fixés. Ainsi, le coefficient de consanguinité peut être vu comme un compromis. Les effets délétères associés à la consanguinité commencent à être observés lorsque le coefficient de consanguinité est supérieur à 5 %, c’est-à-dire juste un peu en dessous de la valeur du coefficient de consanguinité d’un croisement entre deux cousins (=6,25 %).
Une valeur de coefficient de consanguinité élevée augmentera les risques d’expression des effets nuisibles de la consanguinité (dépression de la consanguinité). Par contre, ce même coefficient de consanguinité élevé permet aussi d’augmenter les chances que les traits désirables en lien avec la race en question soient fixés. Ainsi, le coefficient de consanguinité peut être vu comme un compromis. Les effets délétères associés à la consanguinité commencent à être observés lorsque le coefficient de consanguinité est supérieur à 5 %, c’est-à-dire juste un peu en dessous de la valeur du coefficient de consanguinité d’un croisement entre deux cousins (=6,25 %).
Il est conseillé de maintenir un coefficient de consanguinité inférieur à 10 % ce qui devrait permettre de garder stable (fixer) un certain nombre de traits désirables sans toutefois que les effets nuisibles de la consanguinité soient trop prononcés. Ainsi, il faut éliminer les croisements incestueux, avec un coefficient de consanguinité plus élevé que 12,5 %, par exemple les accouplements entre un parent et son enfant, entre un frère et une sœur, entre un grand-parent et son petit-enfant et entre un demi-frère et une demi-sœur. En pratique, il est recommandé de choisir un croisement qui va donner une valeur de coefficient de consanguinité qui est inférieure au coefficient de consanguinité moyen de la race en question. Si plusieurs possibilités de croisements qui donnent un coefficient inférieur à la moyenne sont disponibles, il faut idéalement choisir celui qui donne le coefficient de consanguinité le plus bas, toujours en gardant les traits désirés de la race.
 Ce n’est que très récemment dans la relation homme-chien que les races de chiens pures modernes ont été développées. Au cours des 200 dernières années, les éleveurs canins amateurs en Angleterre ont pris l’exemple des éleveurs de volailles et de bovins pour développer les clubs d’élevages canins. Ce fut aussi le début de la reproduction entre différentes races naturelles (races de fondation) canines via l’hybridation « crossbreeding », afin de créer des mélanges regroupant plusieurs caractéristiques désirées provenant de différentes races en un seul chien ou une seule lignée. Il y eut par la suite une vague intense de reproduction parmi un petit nombre de chiens de la même lignée via la consanguinité « inbreeding », dans l’optique de « réparer » ou de « fixer » les traits de types désirables dans les élevages. Ces traits désirables étaient basés sur une combinaison de caractéristiques physiques et comportementales et sur l’originalité des attributs de l’animal.
Ce n’est que très récemment dans la relation homme-chien que les races de chiens pures modernes ont été développées. Au cours des 200 dernières années, les éleveurs canins amateurs en Angleterre ont pris l’exemple des éleveurs de volailles et de bovins pour développer les clubs d’élevages canins. Ce fut aussi le début de la reproduction entre différentes races naturelles (races de fondation) canines via l’hybridation « crossbreeding », afin de créer des mélanges regroupant plusieurs caractéristiques désirées provenant de différentes races en un seul chien ou une seule lignée. Il y eut par la suite une vague intense de reproduction parmi un petit nombre de chiens de la même lignée via la consanguinité « inbreeding », dans l’optique de « réparer » ou de « fixer » les traits de types désirables dans les élevages. Ces traits désirables étaient basés sur une combinaison de caractéristiques physiques et comportementales et sur l’originalité des attributs de l’animal.  Les races pures ont été définies par des clubs d’élevage, à l’aide d’une description des traits et caractéristiques désirables (et indésirables) et d’un livre maître des pédigrées. Au début, le livre de pédigrée était ouvert et tous les chiens qui correspondaient à la définition de la race donnée par les clubs d’élevage étaient considérés comme étant de race pure. À un certain moment, le livre de pédigrée s’est fermé. Pour enregistrer un animal dans le livre fermé, il fallait à présent que les deux parents de l’animal en question soient déjà dans le livre. The Kennel Club, le club canin d’Angleterre, fondé en 1873, fut le premier club canin qui a formalisé toute la procédure associée à la documentation des descriptions et des pédigrées des différentes races. Depuis, ce modèle a été repris par la plupart des autres clubs canins à travers le monde. Le livre de pédigrée fermé permet d’assurer la constance et la pureté des traits (le type désiré) pour la race pure en question. Par contre, cette uniformité désirable des traits a un coût génétique. En effet, elle engendre aussi une uniformité de la génétique de ces chiens, ce qui peut devenir problématique. Aller voir la section sur la consanguinité.
Les races pures ont été définies par des clubs d’élevage, à l’aide d’une description des traits et caractéristiques désirables (et indésirables) et d’un livre maître des pédigrées. Au début, le livre de pédigrée était ouvert et tous les chiens qui correspondaient à la définition de la race donnée par les clubs d’élevage étaient considérés comme étant de race pure. À un certain moment, le livre de pédigrée s’est fermé. Pour enregistrer un animal dans le livre fermé, il fallait à présent que les deux parents de l’animal en question soient déjà dans le livre. The Kennel Club, le club canin d’Angleterre, fondé en 1873, fut le premier club canin qui a formalisé toute la procédure associée à la documentation des descriptions et des pédigrées des différentes races. Depuis, ce modèle a été repris par la plupart des autres clubs canins à travers le monde. Le livre de pédigrée fermé permet d’assurer la constance et la pureté des traits (le type désiré) pour la race pure en question. Par contre, cette uniformité désirable des traits a un coût génétique. En effet, elle engendre aussi une uniformité de la génétique de ces chiens, ce qui peut devenir problématique. Aller voir la section sur la consanguinité.